- 고객지원
- 업무안내│제품문의
- 전화번호│02-2081-2510
- Email │support@takara.co.kr
- 업무시간안내
- [ 평 일 ] 09 : 00 ~ 18 : 00 │ [ 점심시간 ] 12 : 00 ~ 13 : 00
- 토·일요일, 공휴일은 휴무입니다.
[Cancer Research] HLA typing

HLA typing in cancer
Human Leukocyte Antigen (HLA)은 높은 다형성을 가지며, 면역 조절에 관여하는 유전자다. 이런 HLA typing은 암의 발병이나 재발에 관여하는 돌연변이 등을 확인할 수 있어 매우 중요하다. 주로, 백혈병 (leukemia), 림프종 (lymphoma), 다발성 골수종 (multiple myeloma), 신경 모세포종 (neuroblastoma)과 같은 암의 치료를 위해 장기나 동종의 줄기세포를 이식하기 전에 기증자와 환자 간의 적합성 여부를 확인할 때 사용한다.
NGS (Next-Generation Sequencing)는 HLA typing을 위한 가장 최신의 기술로서, LD PCR과 같이 기존에 사용되던 기술에 비해 낮은 비용으로 더 정확한 결과를 제공한다 (Hosomichi et al. 2015). NGS를 이용한 HLA typing은 복잡하고 광범위한 DNA를 분석하므로 높은 특이성과 정확성을 필요로 한다. 다카라바이오는 HLA typing을 수행할 수 있는 높은 품질과 성능의 NGS library prep. Kit와 targeted sequencing을 위한 high-fidelity polymerase를 제공하고 있다.
Highlighted products
다카라바이오의 PrimeSTAR® GXL과 Takara LA Taq® DNA polymerase는 높은 정확도와 긴 길이의 DNA 증폭, GC-rich 샘플의 적용성으로 HLA typing을 위한 target sequencing에 이상적인 효소로 여겨져 왔으며, 많은 문헌에서 이를 입증하고 있다 (Liu et al. 2018; Xu, Wang 및 Hong 2017; Yin et al. 2016; Mayor et al. 201; Lan et al. 2015; Ozaki et al. 2013; Ozaki et al. 2015).
뿐만 아니라, PicoPLEX® Single Cell WGA Kit v3와 PicoPLEX® Gold Single Cell DNA-seq kit는 간소화된 실험 과정으로 single cell 수준의 WGA (whole genome amplification)을 가능케 하여, NGS, Sanger, array 등을 이용한 HLA typing에 적용할 수 있다. (그림 1).
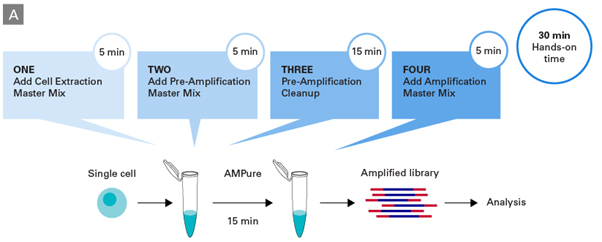
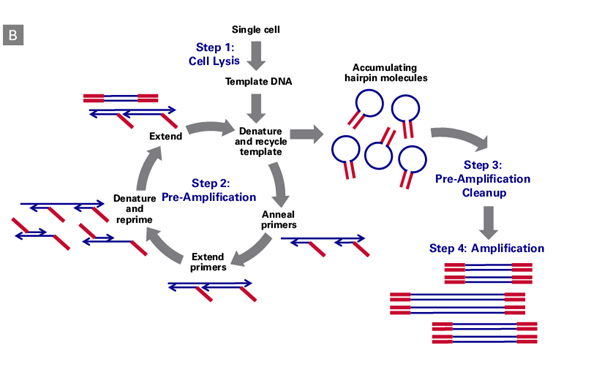
그림 1. PicoPLEX® 기술을 이용한 single cell DNA-seq 과정
(Panel A) Schematic depicting the simple, four-step PicoPLEX® Gold workflow with minimum hands-on time.
(Panel B) Schematic illustrating the PicoPLEX Gold chemistry. Cellular gDNA extracted in Step 1 is used as the template for multiple cycles of quasi-random priming and linear amplification followed by exponential library amplification.
[원문] HLA typing in cancer
[참고문헌] References and product citations
- Hosomichi, K. et al. J. Hum. Genet. 60, 665-673 (2015).
- Lan, J. H. et al. Impact of three Illumina library construction methods on GC bias and HLA genotype calling. Hum. Immunol. 76, 166-175 (2015).
- Liu, C. et al. Accurate typing of human leukocyte antigen class I genes by oxford nanopore sequencing. J. Mol. Diagn. 2, 006 (2018).
- Mayor, N. P. et al. HLA typing for the next generation. PLOS ONE 10, e0127153 (2015).
- Murphy, N. M. et al. Haplotyping the human leukocyte antigen system from single chromosomes. Sci. Rep. 6, 30381 (2016).
- Png, E. et al. A genome-wide association study of hepatitis B vaccine response in an Indonesian population reveals multiple independent risk variants in the HLA region. Hum. Mol. Genet. 20, 3893-3898 (2011).
- Ozaki, Y. et al. HLA-DRB1, -DRB3, -DRB4 and -DRB5 genotyping at a super-high resolution level by long-range PCR and high-throughput sequencing. Tissue Antigens 83, 10-16 (2013).
- Ozaki, Y. et al. Cost-efficient multiplex PCR for routine genotyping of up to nine classical HLA loci in a single analytical run of multiple samples by next-generation sequencing. BMC Genomics 16, 318 (2015).
- Xu, Y.-P., Wang, S.-X. & Hong, W.-X. A novel HLA-E allele, HLA-E*01:01:01:06 , identified in a Chinese Leukemia patient. HLA 89, 260-262 (2017).
- Yin, Y. et al. Application of high-throughput next-generation sequencing for HLA typing on buccal extracted DNA: results from over 10,000 donor recruitment samples. PLoS One 11, e0165810 (2016).
Human Leukocyte Antigen (HLA)은 높은 다형성을 가지며, 면역 조절에 관여하는 유전자다. 이런 HLA typing은 암의 발병이나 재발에 관여하는 돌연변이 등을 확인할 수 있어 매우 중요하다. 주로, 백혈병 (leukemia), 림프종 (lymphoma), 다발성 골수종 (multiple myeloma), 신경 모세포종 (neuroblastoma)과 같은 암의 치료를 위해 장기나 동종의 줄기세포를 이식하기 전에 기증자와 환자 간의 적합성 여부를 확인할 때 사용한다.
NGS (Next-Generation Sequencing)는 HLA typing을 위한 가장 최신의 기술로서, LD PCR과 같이 기존에 사용되던 기술에 비해 낮은 비용으로 더 정확한 결과를 제공한다 (Hosomichi et al. 2015). NGS를 이용한 HLA typing은 복잡하고 광범위한 DNA를 분석하므로 높은 특이성과 정확성을 필요로 한다. 다카라바이오는 HLA typing을 수행할 수 있는 높은 품질과 성능의 NGS library prep. Kit와 targeted sequencing을 위한 high-fidelity polymerase를 제공하고 있다.
Highlighted products
다카라바이오의 PrimeSTAR® GXL과 Takara LA Taq® DNA polymerase는 높은 정확도와 긴 길이의 DNA 증폭, GC-rich 샘플의 적용성으로 HLA typing을 위한 target sequencing에 이상적인 효소로 여겨져 왔으며, 많은 문헌에서 이를 입증하고 있다 (Liu et al. 2018; Xu, Wang 및 Hong 2017; Yin et al. 2016; Mayor et al. 201; Lan et al. 2015; Ozaki et al. 2013; Ozaki et al. 2015).
뿐만 아니라, PicoPLEX® Single Cell WGA Kit v3와 PicoPLEX® Gold Single Cell DNA-seq kit는 간소화된 실험 과정으로 single cell 수준의 WGA (whole genome amplification)을 가능케 하여, NGS, Sanger, array 등을 이용한 HLA typing에 적용할 수 있다. (그림 1).


그림 1. PicoPLEX® 기술을 이용한 single cell DNA-seq 과정
(Panel A) Schematic depicting the simple, four-step PicoPLEX® Gold workflow with minimum hands-on time.
(Panel B) Schematic illustrating the PicoPLEX Gold chemistry. Cellular gDNA extracted in Step 1 is used as the template for multiple cycles of quasi-random priming and linear amplification followed by exponential library amplification.
Code |
제품명 |
용량 |
R050A |
250 U |
|
RR002A |
125 U |
|
R300718 |
24 회 |
|
R300669 |
24 회 |
[원문] HLA typing in cancer
[참고문헌] References and product citations
- Hosomichi, K. et al. J. Hum. Genet. 60, 665-673 (2015).
- Lan, J. H. et al. Impact of three Illumina library construction methods on GC bias and HLA genotype calling. Hum. Immunol. 76, 166-175 (2015).
- Liu, C. et al. Accurate typing of human leukocyte antigen class I genes by oxford nanopore sequencing. J. Mol. Diagn. 2, 006 (2018).
- Mayor, N. P. et al. HLA typing for the next generation. PLOS ONE 10, e0127153 (2015).
- Murphy, N. M. et al. Haplotyping the human leukocyte antigen system from single chromosomes. Sci. Rep. 6, 30381 (2016).
- Png, E. et al. A genome-wide association study of hepatitis B vaccine response in an Indonesian population reveals multiple independent risk variants in the HLA region. Hum. Mol. Genet. 20, 3893-3898 (2011).
- Ozaki, Y. et al. HLA-DRB1, -DRB3, -DRB4 and -DRB5 genotyping at a super-high resolution level by long-range PCR and high-throughput sequencing. Tissue Antigens 83, 10-16 (2013).
- Ozaki, Y. et al. Cost-efficient multiplex PCR for routine genotyping of up to nine classical HLA loci in a single analytical run of multiple samples by next-generation sequencing. BMC Genomics 16, 318 (2015).
- Xu, Y.-P., Wang, S.-X. & Hong, W.-X. A novel HLA-E allele, HLA-E*01:01:01:06 , identified in a Chinese Leukemia patient. HLA 89, 260-262 (2017).
- Yin, Y. et al. Application of high-throughput next-generation sequencing for HLA typing on buccal extracted DNA: results from over 10,000 donor recruitment samples. PLoS One 11, e0165810 (2016).